我院黄林团队发现一系列重要规律仅通过序列即能准确预测一种RNA motif的折叠与结构构象,为推进与提高以序列为基础预测RNA分子结构的计算方法提供了理论与实践基础
【研究背景】
当前蛋白质结构预测发展迅猛且取得极大进展,然而RNA结构预测还存在很多困难,其中重要一点是RNA三维结构的重要组成RNA motif研究少,且从中提取的折叠与结构规律不足。
非编码RNA(ncRNA)与基因的表达调控是当前生命科学最活跃的前沿研究之一。为了理解ncRNA功能,研究RNA的折叠过程与三维结构就显得尤为重要。
K-转角(k-turn)是一类广泛存在于包括核糖体、核糖开关、snoRNA以及lncRNA等的关键结构元件RNA motif,在体内发挥重要作用(图一)。

【主要发现】
在本研究中,黄林课题组发现一系列重要的规律,基于这些规律仅通过序列即能准确预测k-转角在溶液状态下能否正确折叠以及原子尺度精确的结构构象(图一)。将相关规律应用于Breaker 实验室发现的 224 种结构化RNA中,从而鉴定出四个可能的 k-转角(图二),根据相关规则预测其折叠和三维结构。
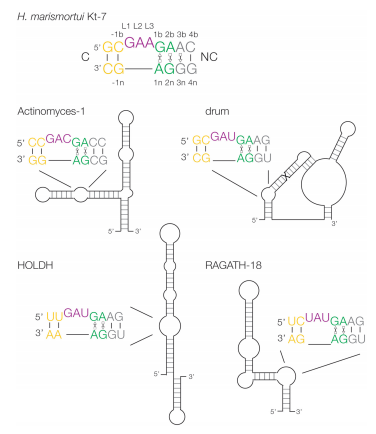
通过荧光共振能量转移(FRET)分析四个k-转角折叠的离子依赖性,并用X-射线晶体学确定了其中两个k-转角的构象,发现实验数据完全符合预测的折叠和三维结构特性。总之,我们的预测规则是可靠而准确的,可以很好的应用于RNA结构预测中。
【研究意义】
本研究是整合各方资源系统研究RNA motif的典型代表,公认为研究最为透彻RNA motif,仅通过序列即能准确预测k-转角的折叠与结构构象。因此,为推进与提高以序列为基础预测RNA分子结构的计算方法提供了理论与实践基础。
论文链接: https://doi.org/10.1093/nar/gkab333
通讯作者:黄林等
第一作者:黄林;李梦筱等






 粤公网安备 44010402003003号
粤公网安备 44010402003003号 